Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
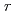 -process nucleosynthesis
-process nucleosynthesisBhattacharyya, A.*; Datta, U.*; Rahaman, A.*; Chakraborty, S.*; Aumann, T.*; Beceiro-Novo, S.*; Boretzky, K.*; Caesar, C.*; Carlson, B. V.*; Catford, W. N.*; et al.
Physical Review C, 104(4), p.045801_1 - 045801_14, 2021/10
被引用回数:5 パーセンタイル:62.78(Physics, Nuclear)中性子過剰核に対する中性子捕獲断面積は、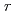 過程元素合成を理解する上で直接必要なデータであるものの、中性子標的が存在しないことと中性子過剰核の半減期が短いため、その実験を行うことは困難である。その代替手段として、
過程元素合成を理解する上で直接必要なデータであるものの、中性子標的が存在しないことと中性子過剰核の半減期が短いため、その実験を行うことは困難である。その代替手段として、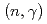 反応の逆過程である
反応の逆過程である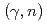 反応のデータから導出する方法が行われている。本論文では、中性子数20領域の中性子過剰核に対し、クーロン分解反応を用いて
反応のデータから導出する方法が行われている。本論文では、中性子数20領域の中性子過剰核に対し、クーロン分解反応を用いて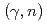 反応の断面積を測定し、そこから
反応の断面積を測定し、そこから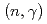 反応の断面積を得た。その結果、
反応の断面積を得た。その結果、 Naと
Naと Alに対する中性子捕獲断面積については、統計模型で予測された値よりも小さく、
Alに対する中性子捕獲断面積については、統計模型で予測された値よりも小さく、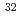 Mgに対しては大きな値となることがわかった。
Mgに対しては大きな値となることがわかった。
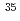 Al via Coulomb breakup
Al via Coulomb breakupChakraborty, S.*; Datta, U.*; Aumann, T.*; Beceiro-Novo, S.*; Boretzky, K.*; Caesar, C.*; Carlson, B. V.*; Catford, W. N.*; Chartier, M.*; Cortina-Gil, D.*; et al.
Physical Review C, 96(3), p.034301_1 - 034301_9, 2017/09
被引用回数:4 パーセンタイル:34.33(Physics, Nuclear)GSIのLAND-FRSセットアップを用いて、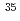 Alの基底状態配位をクーロン分解反応によって調べた。そこで得られた包括的断面積は78(13)mbとなった。単一粒子模型によるクーロン分解反応断面積を大規模殻模型計算による
Alの基底状態配位をクーロン分解反応によって調べた。そこで得られた包括的断面積は78(13)mbとなった。単一粒子模型によるクーロン分解反応断面積を大規模殻模型計算による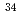 Al+1中性子系の分光学的因子と組み合わせることによって得られた理論計算の断面積を実験値と比較した。その結果、殻模型計算では
Al+1中性子系の分光学的因子と組み合わせることによって得られた理論計算の断面積を実験値と比較した。その結果、殻模型計算では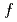 軌道の寄与をいくらか過大評価し、
軌道の寄与をいくらか過大評価し、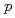 軌道の寄与を過小評価していることがわかった。これは、
軌道の寄与を過小評価していることがわかった。これは、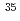 Alの基底状態において中性子数28の殻ギャップが著しく縮まっており、それによって、
Alの基底状態において中性子数28の殻ギャップが著しく縮まっており、それによって、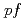 殻を占める最後の2個の中性子軌道が
殻を占める最後の2個の中性子軌道が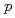 軌道をより多く占有しているためであると考えられる。
軌道をより多く占有しているためであると考えられる。
Jacquinot, J.*; Albajar, F.*; Beaumont, B.*; Becoulet, A.*; Bonicelli, T.*; Bora, D.*; Campbell, D.*; Chakraborty, A.*; Darbos, C.*; Decamps, H.*; et al.
Fusion Engineering and Design, 84(2-6), p.125 - 130, 2009/06
被引用回数:24 パーセンタイル:82.15(Nuclear Science & Technology)ITER用電子サイクロトロン波(EC),イオンサイクロトロン波(IC),中性ビーム(NB)、そして低域混成波(LH)について、その物理と工学の両面の進展を2007/2008年にレビューした。全体仕様の変更はないものの、以下のような設計変更があった。第一に、DTフェーズの前に全パワーである73MW入射をルーティンに入射可能となるように調整すべきこと。第二に、NBを水素フェーズにもフルパワー入射が可能となるように対向壁を用意する、IC用によりロバスト名アンテナ2式を用意する、またECには2MW容量の伝送系を用意して、増力を容易にする。さらにRF源と計測及び加熱用ポートプラグの試験施設となる付属建屋を用意する。第三に、LHのようにITERの長パルス運転時に適した電流駆動システムを開発するための計画の必要性が認識された。
山崎 千里*; 村上 勝彦*; 藤井 康之*; 佐藤 慶治*; 原田 えりみ*; 武田 淳一*; 谷家 貴之*; 坂手 龍一*; 喜久川 真吾*; 嶋田 誠*; et al.
Nucleic Acids Research, 36(Database), p.D793 - D799, 2008/01
被引用回数:52 パーセンタイル:71.76(Biochemistry & Molecular Biology)ヒトゲノム解析のために、転写産物データベースを構築した。34057個のタンパク質コード領域と、642個のタンパク質をコードしていないRNAを見いだすことができた。