Structural comparison of the substrate-binding mechanism between maltooligosyl trehalose synthase (MTSase) and maltooligosyl trehalose trehalohydrolase (MTHase)
マルトオリゴシルトレハロース合成酵素とマルトオリゴシルトレハローストレハロヒドロラーゼ間の基質結合部位の構造的比較
安達 基泰; 岡崎 伸生*; 玉田 太郎; 加藤 優*; 小林 和男*; Blaber, M.; 黒木 良太
Adachi, Motoyasu; Okazaki, Nobuo*; Tamada, Taro; Kato, Masaru*; Kobayashi, Kazuo*; Blaber, M.; Kuroki, Ryota
マルトオリゴシルトレハロース合成酵素(MTSase)とマルトオリゴシルトレハローストレハロヒドロラーゼ(MTHase)は、食品の保存料として実用的な化合物であるトレハロースを効率的に生産するために鍵となる酵素である。今回、前者のMTSaseの触媒機構を理解するために、超高熱古細菌MTSaseのSulfolobus shibatae DSM5389由来のMTSaseのX線結晶構造を2.3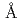 の分解能で決定した。その結果、(
の分解能で決定した。その結果、(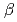 /
/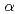 )8ドメインに存在するAsp241, Glu269, Asp460の3つの残基が、関連酵素において普遍的に存在する触媒残基であることがわかった。
)8ドメインに存在するAsp241, Glu269, Asp460の3つの残基が、関連酵素において普遍的に存在する触媒残基であることがわかった。
Maltooligosyl trehalose synthase (MTSase) and maltooligosyl trehalose trehalohydrolase (MTHase) are key enzymes for effective production of trehalose which is a useful compound as a preservative for foods. To understand the catalytic mechanism of MTSase, the crystal structure of MTSase derived from the hyperthermophilic archaeum Sulfolobus shibatae DSM5389 has been determined to 2.3 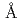 resolution by X-ray crystallography. Three invariant catalytic carboxylic amino acids in the
resolution by X-ray crystallography. Three invariant catalytic carboxylic amino acids in the 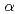 -amylase family are found in MTSase at positions Asp241, Glu269 and Asp460 in the (
-amylase family are found in MTSase at positions Asp241, Glu269 and Asp460 in the (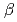 /
/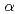 )8 domain.
)8 domain.